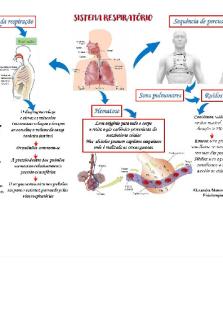
Mapa mental sobre replicação do DNA PDF

| Title | Mapa mental sobre replicação do DNA |
|---|---|
| Author | Marcelo Brandt |
| Course | Genética Geral |
| Institution | Universidade Federal Rural de Pernambuco |
| Pages | 2 |
| File Size | 150.4 KB |
| File Type | |
| Total Downloads | 117 |
| Total Views | 155 |
Summary
mapa mental sobre Replicação do DNA de acordo com a aula do prof. Martin Alejandro Montes....
Description
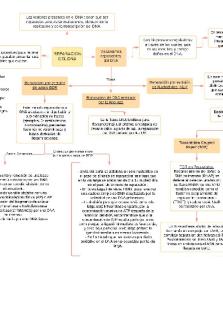
através de um experimento com o isótopo do nitrogênio (15N), concluiu-se que a replicação ocorria de forma semiconservativa. Os pesquisadores analisaram os pesos moleculares das moléculas de DNA recémsintetizadas e observaram que as novas cadeias apresentavam pesos correspondentes a uma replicação semiconservativa (uma fita pesada e uma fita leve).
Se imaginavam 3 possibilidades para os tipos de replicação: conservativa, semiconservativa e dispersiva. Foi definido através do experimento de meselson e stahl que a forma correta é a replicação semiconservativa.
Experimento de Meselson e Stahl
Origem de replicação: regiões onde se inicia a duplicação de DNA. Procariontes = uma origem; Eucariontes = Vários elementos SRA (sequências de replicação autônomas)
Replicação Semiconservativa
Cada nova molécula é composta por uma fita parental e uma fita recém-sintetizada: configurando a replicação semiconservativa.
Processo de Replicação
Ocorre de forma simultânea e ordenada.
Formação da Forquilha de Replicação
Replicação do DNA
Formado pela interação entre o complexo proteico (DNA polimerase, helicase, primase, ligase, etc) e as origens
a partir das forquilhas, os complexos proteicos par sentidos opostos. Cada bolha é responsável pela polimerização de uma parte do DNA chamada de r
Separação das fitas parentais de uma molécula de DNA e a produção de duas novas fitas, tendo as fitas parentais como molde.
Iniciação da Replicação
Separação das Fitas
A dupla fita é desnaturada pela enzima DNA helicase as enzimas DNA girase rompem as ligações fosfodiéster e permitem o giro das fitas, deixando-as aptas para a replicação
As Polimerases (enzimas que replicam o DNA de fato) precisam de um primer para inicializar a síntese. O primer é produzido por um complexo chamado primossomo, que apresenta uma RNA polimerase como principal constituinte. O primer principalmente fornece uma hidroxila livre ao carbono 3', necessária para o início do trabalho das polimerases.
Polimerização A orientação antiparalela da cadeia dupla e a incapacidade das enzimas em polimerizar no sentido 3’ -> 5’ faz com que uma das novas fitas ocorra normalmente de forma contínua pois segue o sentido 5’ -> 3’ e não precisa de mais de um iniciador; Enquanto a fita 3’ -> 5’ será sintetizada em pedaços descontínuos com cerca de 1.000 a 2.000 nucleotídeos nos procariontes e 100 a 200 nos eucariontes. Esses pedaços descontínuos são denominados fragmentos de Okazaki. Cada fragmento é formado a partir de um primer e é alongado no sentido 5’→3. Posteriormente os primers que estão interrompendo os fragmentos de Okazaki na fita descontínua serão removidos e substituídos por outros nucleotídeos.
Após a produção dos primers, as DNA polimerases podem iniciar a replicação. Existem várias DNA polimerases: nos procariontes principalmente as I, II e III e nos eucariontes principalmente as alfa, beta, gama, delta e epsilon. Algumas são responsáveis pelo reparo do DNA, e as responsáveis pela replicação são as II e III e alfa e delta.
Fragmento de Okazaki
Finalização e Ligase
O conjunto de enzimas (polimerases, helicases, topoisomerases, primases, ligases, etc) formam o replissomo, uma unidade que adiciona nucleotídeos a fita em formação de forma conseguinte. Sempre acontece no sentido 5' -> 3'.
Para a finalização do processo, a enzima DNA ligase fará a união dos fragmentos de Okazaki aos nucleotídeos recémadicionados através de ligações fosfodiéster. O filamento contínuo possui apenas um primer que também será
substituído pela DNA polimerase....
Similar Free PDFs
Reparación del DNA - Mapa mental
- 1 Pages

Atividade do Mapa mental
- 2 Pages

Síntese do mapa mental
- 2 Pages

Mapa mental sobre Vygotsky
- 1 Pages

MAPA Mental Fisiologia DO Cálcio
- 1 Pages
Popular Institutions
- Tinajero National High School - Annex
- Politeknik Caltex Riau
- Yokohama City University
- SGT University
- University of Al-Qadisiyah
- Divine Word College of Vigan
- Techniek College Rotterdam
- Universidade de Santiago
- Universiti Teknologi MARA Cawangan Johor Kampus Pasir Gudang
- Poltekkes Kemenkes Yogyakarta
- Baguio City National High School
- Colegio san marcos
- preparatoria uno
- Centro de Bachillerato Tecnológico Industrial y de Servicios No. 107
- Dalian Maritime University
- Quang Trung Secondary School
- Colegio Tecnológico en Informática
- Corporación Regional de Educación Superior
- Grupo CEDVA
- Dar Al Uloom University
- Centro de Estudios Preuniversitarios de la Universidad Nacional de Ingeniería
- 上智大学
- Aakash International School, Nuna Majara
- San Felipe Neri Catholic School
- Kang Chiao International School - New Taipei City
- Misamis Occidental National High School
- Institución Educativa Escuela Normal Juan Ladrilleros
- Kolehiyo ng Pantukan
- Batanes State College
- Instituto Continental
- Sekolah Menengah Kejuruan Kesehatan Kaltara (Tarakan)
- Colegio de La Inmaculada Concepcion - Cebu